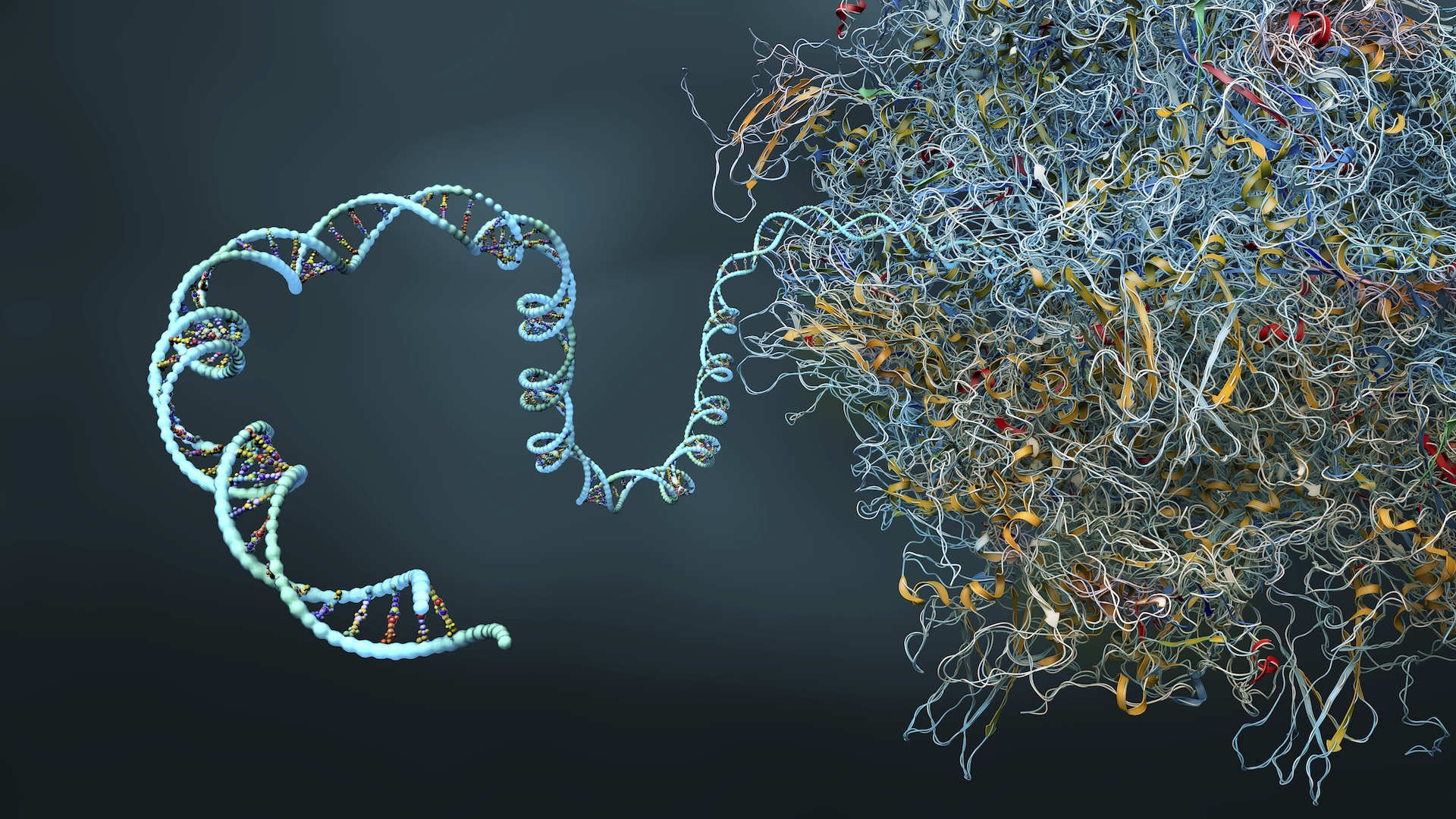
Les chercheurs d’IBM et Moderna ont utilisé avec succès un algorithme de simulation quantique pour prédire la structure des protéines secondaires complexes d’un 60 nucléotide ARNm séquence, la plus longue jamais simulée sur un ordinateur quantique.
Acide ribonucléique messager (ARNm) est une molécule qui porte des informations génétiques de l’ADN aux ribosomes. Il dirige la synthèse des protéines dans les cellules et est utilisé pour Créer des vaccins efficaces capable d’inciter des réponses immunitaires spécifiques.
C’est largement cru Le fait que toutes les informations requises pour qu’une protéine adopte la conformation tridimensionnelle correcte soit fournie par sa séquence d’acides aminés ou le «pliage».
Bien qu’il ne soit composé qu’un seul brin d’acides aminés, l’ARNm a une structure protéique secondaire composée d’une série de plis qui fournissent une forme 3D spécifique d’une molécule donnée. Le nombre de permutations pliantes possibles augmente de façon exponentielle avec chaque nucléotide ajouté. Cela rend le défi de prédire la forme qu’une molécule d’ARNm prendra insoluble à des échelles plus élevées.
L’expérience IBM et Moderna, décrite dans un étude Publié pour la première fois pour la Conférence internationale de l’IEEE 2024 sur l’informatique quantique et l’ingénierie, a démontré comment l’informatique quantique peut être utilisée pour augmenter les méthodes traditionnelles pour faire de telles prédictions. Traditionnellement, ces prédictions généralement invoqué sur Ordinateurs binaires et classiques et intelligence artificielle (AI) des modèles tels que Google Alphafold de Deepmind.
Selon une nouvelle étude publiée le 9 mai sur la préimpression arxiv La base de données, les algorithmes capables de fonctionner sur ces architectures classiques peuvent traiter des séquences d’ARNm avec « des centaines ou des milliers de nucléotides », mais uniquement en excluant des caractéristiques de complexité plus élevées telles que « pseudoknots ».
Les pseudoknots sont des rebondissements et des formes complexes dans la structure secondaire d’une molécule qui sont capables de s’engager Interactions internes plus complexes que les plis ordinaires. Grâce à leur exclusion, la précision potentielle de tout modèle de prédiction de repliement des protéines est fondamentalement limitée.
Comprendre et prédire même les plus petits détails des plis protéiques d’une molécule d’ARNm est intrinsèque pour développer des prédictions plus fortes et, par conséquent, vaccins basés sur l’ARNm plus efficaces.
Les scientifiques espèrent surmonter les limites inhérentes à Supercomputeurs les plus puissants et les modèles d’IA en augmentant des expériences avec la technologie quantique. Les chercheurs ont mené plusieurs expériences à l’aide d’algorithmes de simulation quantique qui s’appuyaient sur qubits – L’équivalent quantique d’un bit d’ordinateur – pour modéliser les molécules.
En utilisant initialement seulement 80 qubits (sur un possible 156) sur le Heron R2 unité de traitement quantique (QPU) ,, L’équipe a utilisé un algorithme quantique variationnel de valeur conditionnelle basée sur le risque (VQA basé sur CVAR) – un algorithme d’optimisation quantique modélisé après certaines techniques utilisées pour analyser les interactions complexes telles que Évitement des collisions et techniques d’évaluation des risques financiers – pour prédire la structure protéique secondaire d’une séquence d’ARNm de 60 nucléotides.
Le meilleur précédent pour un modèle de simulation basé sur quantique, Selon l’étudeétait une séquence de 42 nucléotides. Les chercheurs ont également mis à l’échelle l’expérience en appliquant Techniques de correction des erreurs récentes pour gérer le bruit généré par les fonctions quantiques.
Dans la nouvelle étude de préparation, l’équipe a provisoirement démontré l’efficacité du paradigme expérimental dans l’exécution des instances simulées avec jusqu’à 156 qubits pour des séquences d’ARNm allant jusqu’à 60 nucléotides. Ils ont également mené des recherches préliminaires démontrant le potentiel d’emplacement jusqu’à 354 Qubits pour les mêmes algorithmes dans des contextes sans bruit.
En apparence, l’augmentation du nombre de qubits utilisées pour exécuter l’algorithme, tout en augmentant les algorithmes pour des sous-programmes supplémentaires, devrait conduire à des simulations plus précises et à la capacité de prédire des séquences plus longues, ont-ils déclaré.
Ils ont cependant noté que «ces méthodes nécessitent le développement de techniques avancées pour intégrer ces circuits spécifiques au problème dans le matériel quantique existant», indiquant que de meilleurs algorithmes et architectures de traitement seront nécessaires pour faire avancer la recherche.